1
2
3
4
5
6
7
8
9
10
11
12
13
14
15
16
17
18
19
20
21
22
23
24
25
26
27
28
29
30
31
32
33
34
35
36
37
38
39
40
| # Modèle réponse immunitaire à un développement de cellules cancéreuses
# paramètres du code
parameters <- c(
a= 5.14*10^-1 # vitesse de croissance de la tumeur (day^-1)
b= 1.02*10^-9 #
c=3.23*10^-7
d=1.43
lamda=5.8*10^-1
s=2.73
sigma=1.3*10^4
f=4.12*10^-2
g=2.5*10^-2
h=2.02*10^7
m=2*10^-2
j=3.75*10^-2
k=2.02*10^7
q=3.42*10^-10
r=1.1*10^-7
)
# valeurs initiales du problème
initial-conditions=c( N0=0,
L(0)=0,
T(0)=0
)
cell-cell <- function(t, state, parameters) {
with(as.list(c(state, parameters)), {
dT <- a*T*(1-b*T)-c*N*T-D
dN <- sigma-f*N+((g*T*T)/(h+T^2))-p*N*T
dL <- -m*L+((j*D*D)/(k+D^2))*L-q*L*T+r*n*T
D=d*((L/T)^lamda)/(s+(L/T)^lamda))*T
list(c(dT, dN, dL,D))
})
}
state <- c(???)
times <- seq(0,40, by = 0.1)
out <- ode(y = state, times = times, func = cell-cell, parms = parameters)
plot(out) |
On nous a donné un projet où on doit programmer sur R et moi c'est la première fois que j'utilise ce logiciel et déjà je suis pas très familière à la modélisation par logiciels !









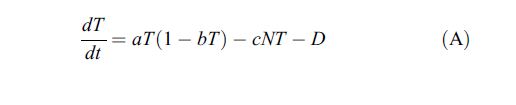
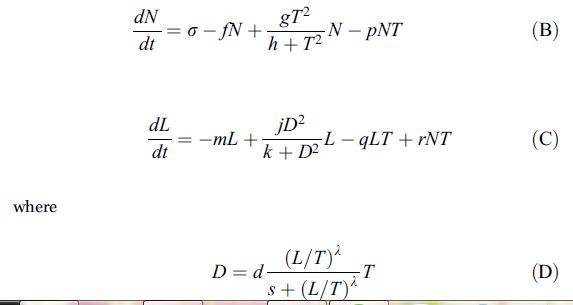
 Répondre avec citation
Répondre avec citation
Partager