Bonjour,
j'ai les données suivantes:
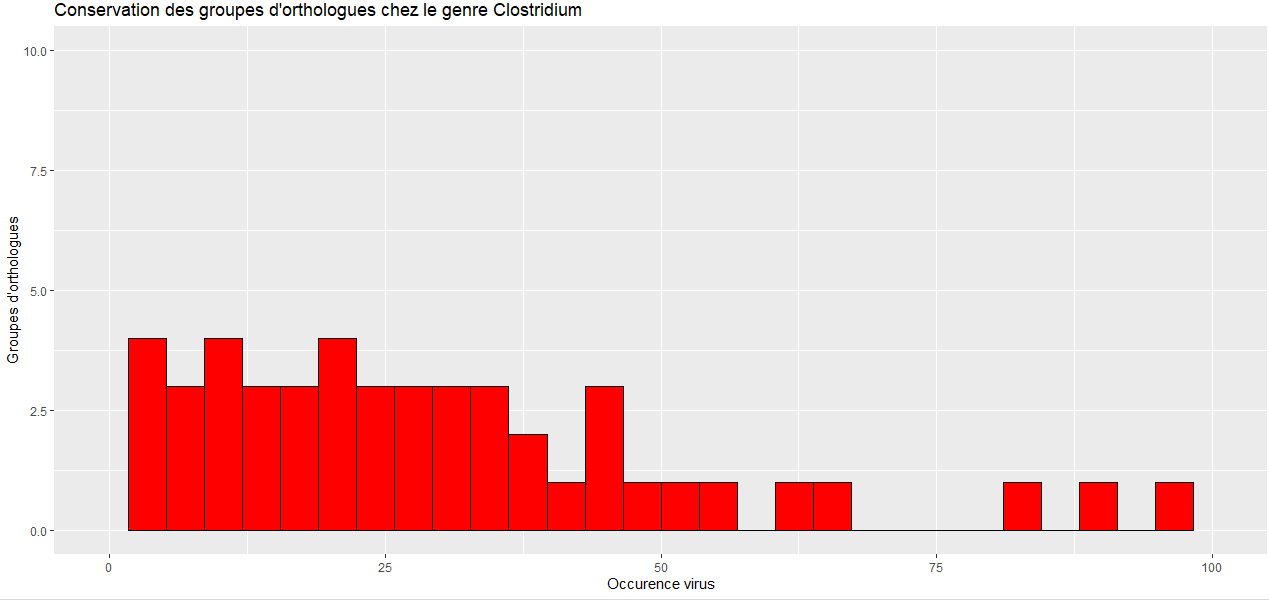
Clostridium occurence virus Clostridium Groupes orthologues 53 1 61 1 98 1 3 196 83 1 44 1 91 1 42 1 46 1 11 22 45 2 7 28 12 7 4 106 2 531 6 43 37 1 1 2196 16 8 18 2 56 1 66 1 32 2 34 2 5 87 20 4 13 9 21 2 14 8 48 1 8 31 35 1 15 5 29 2 33 2 31 3 23 3 19 4 39 1 10 16 22 1 26 4 17 2 24 2 28 1 9 13 30 1 25 1
et j'essai de représenter ces données sous forme d'histogramme sans succès...
Voici mon code R actuel :
et j'obtiens cela :
Code : Sélectionner tout - Visualiser dans une fenêtre à part
2
3
4
5
6
7
8
9
10
11
12
13
Comme vous pouvez le constater dans les données, j'ai 2196 groupes d'orthologues contenant 1 virus...alors que dans mon graphiques les barres ne vont pas plus haut que environ 4...
Pouvez vous m'aider à construire un histogramme convenable pour représenter ces données svp ?
Merci à vous









 Répondre avec citation
Répondre avec citation



Partager